理研 並列化のサマースクール
-
- 自分のモチベーションとしては、シミュレーションなどを通じて”並列化”という言葉は知っていたが、全くの無勉強であり、講習会を導入として習おうということ
平衡点を求める
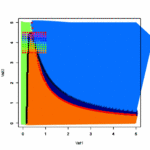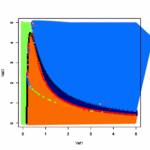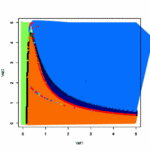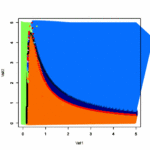
- 状態の変化を表した式から平衡状態を求めたい
- 1次元のブリュッセレータで試してみる
- パッケージrootSolveの中のmultiroot関数を使う
- multirootの中身でもRの逆行列(solve)をつかっているようだ
- 黒がX、赤がYの濃度
- 解が安定かどうかはたぶんまた別のはなし
- 解の一意性も別のはなし
- 初期条件をいろいろ変えてみる必要がありそう
- 計算の時間の刻み幅(dt)の値で結果が変わってしまうので拡散係数の修正が必要
- こちらのような数値計算で方程式の解をだせるようにしたい
library(rootSolve) # ブリュッセレータのパラメータ A<-2 B<-4.17 X0<-c(A,B/A) # 平衡となるXとYの値 # シミュレーションのパラメータ L<-1 dr<-0.01 Nr<-floor(L/dr)+1 dt<-0.00001 # 拡散係数 Dx<-0.0016 Dy<-0.008 # 各点のX,Yの濃度、初期条件 C<-matrix(X0,nr=2,nc=Nr) Nint<-2 C<-C+c(sin(Nint*pi*1:Nr/(L*Nr)),sin(Nint*pi*1:Nr/(L*Nr))) # 初期条件 C[,1]<-C[,Nr]<-X0 #固定端 par(mfrow=c(1,2)) plot(seq(from=0,to=1,length=Nr),C[1,],type="l",xlab="r",ylab="X conc.",ylim=range(C),main="initial concentration") par(new=T) plot(seq(from=0,to=1,length=Nr),C[2,],type="l",xlab="r",ylab="Y conc.",ylim=range(C),main="initial concentration",col=2) # ブリュッセレータ f<-function(X){ Y<-c(0,0) Y[1] <- A+X[1]^2*X[2]-B*X[1]-X[1] Y[2] <- B*X[1]-X[1]^2*X[2] return(Y) } # ブリュッセレータと拡散 h<-function(C){ C<-matrix(C,nr=2,nc=Nr) C0<-C # ブリュッセレータの計算 for(l in 1:Nr) { X<-C[,l] dX<-f(X)*dt C[,l]<-X+dX } # 拡散の計算 dC_r<-C[,-1]-C[,-Nr] Ir<- -c(Dx,Dy)*dC_r C[,-1]<-C[,-1]+Ir C[,-Nr]<-C[,-Nr]-Ir # 固定端 C[,1]<-C[,Nr]<-X0 return(C-C0) # 変化量をかえす } # パッケージrootSolveの中のmultirootを使う root<-multiroot(h,C,maxiter=100)$root # print(matrix(h(root),nr=2,nc=Nr)) CC<-matrix(root,nr=2,nc=Nr) plot(seq(from=0,to=1,length=Nr),CC[1,],type="l",xlab="r",ylab="X conc.",ylim=range(CC),main=paste(" equilibirium")) par(new=T) plot(seq(from=0,to=1,length=Nr),CC[2,],type="l",xlab="r",ylab="Y conc.",ylim=range(CC),main=paste(" equilibirium"),col=2) # plot(seq(from=0,to=1,length=Nr),h(CC)[1,],type="l",ylim=c(-0.1,0.1),xlab="r",ylab="X conc.",main=paste("flux"))
- 下はシミュレーション用のコード
A<-2 B<-4.17 X0<-c(A,B/A) # 平衡となるXとYの値 L<-1 dr<-0.01 Nr<-floor(L/dr)+1 T<-3 dt<-0.00001 Nt<-T/dt # 拡散係数 Dx<-0.0016 Dy<-0.008 # 各点のX,Yの濃度 C<-matrix(X0,nrow=2,ncol=Nr) Nint<-2 C<-C+c(sin(Nint*pi*1:Nr/(L*Nr)),sin(Nint*pi*1:Nr/(L*Nr))) range<-range(C) plot(seq(from=0,to=1,length=Nr),C[1,],type="l",ylim=range,xlab="r",ylab="X conc.",main="time = 0") par(new=T) plot(seq(from=0,to=1,length=Nr),C[2,],type="l",ylim=range,xlab="r",ylab="Y conc.",main="time = 0",col=2) # ブリュッセレータ f<-function(X){ Y<-c(0,0) Y[1] <- A+X[1]^2*X[2]-B*X[1]-X[1] Y[2] <- B*X[1]-X[1]^2*X[2] return(Y) } for(t in 1:Nt) { # ブリュッセレータの計算 for(l in 1:Nr) { X<-C[,l] dX<-f(X)*dt C[,l]<-X+dX } # 拡散の計算 dC_r<-C[,-1]-C[,-Nr] Ir<- -c(Dx,Dy)*dC_r C[,-1]<-C[,-1]+Ir C[,-Nr]<-C[,-Nr]-Ir # 固定端 C[,1]<-C[,Nr]<-X0 if(t %% 100 == 0){ plot(seq(from=0,to=1,length=Nr),C[1,],type="l",ylim=range,xlab="r",ylab="X conc.",main=paste("time = ",t*dt,sep="")) par(new=T) plot(seq(from=0,to=1,length=Nr),C[2,],type="l",ylim=range,xlab="r",ylab="Y conc.",main=paste("time = ",t*dt,sep=""),col=2) } }
library(fields) # 連立方程式 f<-function(x){ z<-rep(0,dim) z[1]<-(x[1]-3)^2+x[2]^2-3 z[2]<-sin(x[1])+exp(x[2]-1)-1 return(z) } # 偏微分係数を近似計算するときに差分を与える関数 g<-function(i){ v<-rep(0,dim) v[i]<-1 return(v) } d<-0.001 # 偏微分係数の近似のための差分 dim<-2 A<-matrix(0,nr=dim,nc=dim) #ヤコビアン vectors<-c() errors<-c() # 初期値の集合 by<-0.05 x0<-seq(from=0,to=5,by=by) y0<-seq(from=-2.5,to=2.5,by=by) points<-data.matrix(expand.grid(x0,y0)) lx<-length(x0) ly<-length(y0) L<-nrow(points) pmat_x<-matrix(points[,1],lx,ly) pmat_y<-matrix(points[,2],lx,ly) vectors<-points for(l in 1:L){ x<-XY<-points[l,] # ヤコビアンの計算 for(i in 1:dim){ for(j in 1:dim){ A[i,j]<-(f(x+d*g(j))[i]-f(x-d*g(j))[i])/(2*d) }} dXY<- try(-solve(A)%*%f(x)) if(is(dXY)[1] != "try-error"){# 連立方程式が解けた時 vectors[l,]<-dXY }else{ # 連立方程式が解けなかった時 errors<-cbind(errors,XY) vectors[l,]<-c(0,0) # 0 を入れておく } } # ベクトルでプロット #png("vector field.png") plot(points,xlim=range(points[,1]),ylim=range(points[,2]),type="n") arrow.plot(points[,1],points[,2],vectors[,1],vectors[,2],arrow.ex=.2, length=.1,col=tim.colors(5)[(atan2(vectors[,2],vectors[,1])+pi)/(2*pi)*4+1], lwd=2,xlim=range(points[1,]),ylim=range(points[2,])) # dev.off() # 境界を求める vmat_x<-matrix(vectors[,1],lx,ly) vmat_y<-matrix(vectors[,2],lx,ly) bound_x<-(vmat_x[-1,]*vmat_x[-lx,]<0) bound_y<-(vmat_y[,-1]*vmat_y[,-ly]<0) # xの境界 bx_x<-(pmat_x[-1,][bound_x == 1]+pmat_x[-lx,][bound_x == 1])/2 bx_y<-(pmat_y[-1,][bound_x == 1]+pmat_y[-lx,][bound_x == 1])/2 # yの境界 by_x<-(pmat_x[,-1][bound_y == 1]+pmat_x[,-ly][bound_y == 1])/2 by_y<-(pmat_y[,-1][bound_y == 1]+pmat_y[,-ly][bound_y == 1])/2 # どっち? # vmat or vmat * pmat ?? xstable<-(vmat_x[-1,]<0)*(vmat_x[-lx,]>0) xstable_x<-(pmat_x[-1,][xstable == 1]+pmat_x[-lx,][xstable == 1])/2 xstable_y<-(pmat_y[-1,][xstable == 1]+pmat_y[-lx,][xstable == 1])/2 xunstable<-(vmat_x[-1,]>0)*(vmat_x[-lx,]<0) xunstable_x<-(pmat_x[-1,][xunstable == 1]+pmat_x[-lx,][xunstable == 1])/2 xunstable_y<-(pmat_y[-1,][xunstable == 1]+pmat_y[-lx,][xunstable == 1])/2 ystable<-(vmat_y[,-1]<0)*(vmat_y[,-ly]>0) ystable_x<-(pmat_x[,-1][ystable == 1]+pmat_x[,-ly][ystable == 1])/2 ystable_y<-(pmat_y[,-1][ystable == 1]+pmat_y[,-ly][ystable == 1])/2 yunstable<-(vmat_y[,-1]>0)*(vmat_y[,-ly]<0) yunstable_x<-(pmat_x[,-1][yunstable == 1]+pmat_x[,-ly][yunstable == 1])/2 yunstable_y<-(pmat_y[,-1][yunstable == 1]+pmat_y[,-ly][yunstable == 1])/2 # 角度と境界をプロット dev.new() # png("angle.png") par(mfrow=c(2,2)) #1 plot(points,xlim=range(points[,1]),ylim=range(points[,2]),col=tim.colors(501)[(atan2(vectors[,2],vectors[,1])+pi)/(2*pi)*500+1], lwd=2,pch=15,cex=1,main="angle",xlab="X",ylab="Y") #2 plot(points,xlim=range(points[,1]),ylim=range(points[,2]),col=tim.colors(501)[(atan2(vectors[,2],vectors[,1])+pi)/(2*pi)*500+1], lwd=2,pch=15,cex=1,main="merge",xlab="X",ylab="Y") par(new=T) plot(xstable_x,xstable_y,pch=16,xlim=range(points[,1]),ylim=range(points[,2]),xlab="",ylab="") par(new=T) plot(xunstable_x,xunstable_y,pch=3,xlim=range(points[,1]),ylim=range(points[,2]),xlab="",ylab="") par(new=T) plot(ystable_x,ystable_y,pch=16,col="red",xlim=range(points[,1]),ylim=range(points[,2]),xlab="",ylab="") par(new=T) plot(yunstable_x,yunstable_y,pch=3,col="red",xlim=range(points[,1]),ylim=range(points[,2]),xlab="",ylab="") #3 plot(xstable_x,xstable_y,pch=16,xlim=range(points[,1]),ylim=range(points[,2]),main="boundary of x",xlab="X",ylab="Y") par(new=T) plot(xunstable_x,xunstable_y,pch=3,xlim=range(points[,1]),ylim=range(points[,2]),xlab="",ylab="",) #4 plot(ystable_x,ystable_y,pch=16,col="red",xlim=range(points[,1]),ylim=range(points[,2]),main="boundary of y",xlab="X",ylab="Y") par(new=T) plot(yunstable_x,yunstable_y,pch=3,col="red",xlim=range(points[,1]),ylim=range(points[,2]),xlab="",ylab="") # dev.off() # 安定性 dev.new() # png("Stability.png",width=960) par(mfrow=c(1,2)) #1 plot(points,xlim=range(points[,1]),ylim=range(points[,2]),col=tim.colors(501)[ifelse((vmat_x<0),100,500)], lwd=2,pch=15,cex=1,main="x stability",xlab="X",ylab="Y") par(new=T) plot(xstable_x,xstable_y,pch=16,xlim=range(points[,1]),ylim=range(points[,2]),main="",xlab="",ylab="") par(new=T) plot(xunstable_x,xunstable_y,pch=3,xlim=range(points[,1]),ylim=range(points[,2]),xlab="",ylab="") #2 plot(points,xlim=range(points[,1]),ylim=range(points[,2]),col=tim.colors(501)[ifelse((vmat_y<0),100,500)], lwd=2,pch=15,cex=1,main="y stability",xlab="X",ylab="Y") par(new=T) plot(ystable_x,ystable_y,pch=16,col="red",xlim=range(points[,1]),ylim=range(points[,2]),main="",xlab="",ylab="") par(new=T) plot(yunstable_x,yunstable_y,pch=3,col="red",xlim=range(points[,1]),ylim=range(points[,2]),xlab="",ylab="") # dev.off()
- こちらに追加
数値計算
x<-c(0,0) T<-100 d<-0.01 dim<-length(x) f<-function(x){ z<-rep(0,dim) z[1]<-(x[1]-3)^2+x[2]^2-3 z[2]<-sin(x[1])+exp(x[2]-1)-1 return(z) } g<-function(i){ v<-rep(0,dim) v[i]<-1 return(v) } A<-matrix(0,nr=dim,nc=dim) for(t in 1:T){ for(i in 1:dim){ for(j in 1:dim){ A[i,j]<-(f(x+d*g(j))[i]-f(x-d*g(j))[i])/(2*d) }} x<-x-solve(A)%*%f(x) } print(x) print(f(x))
RとCを使う改良版
#include <stdio.h> #include <math.h> #include <stdlib.h> #define PI 3.1415926535 int main (int argc, char *argv[]){ int Nx, Ny, Nz; int i,j,k; FILE *fp; Nx = atoi(argv[1]); Ny = atoi(argv[2]); Nz = atoi(argv[3]); // printf("argv = %d\n",atoi(argv[1])); double A[Nx][Ny][Nz]; for (k = 0; k < Nz; k++) { for (j = 0; j < Ny; j++) { for (i = 0; i < Nx; i++) { A[i][j][k] = (i + 1)*(j + 1)*(k + 1)*1.0; // fp = fopen("Numbers.txt","a"); // if(fp == NULL)return 1; // fprintf(fp,"%f\n",A[i][j][k]); // fclose(fp); }}} fp = fopen("Numbers.txt","wb"); if(fp == NULL){ printf("ファイル操作中にエラー"); exit(1); } fwrite(A,sizeof(double),Nx*Ny*Nz,fp); fclose(fp); return 0; }
- Rのスクリプト
# mat.R library(rgl) Nx <- as.numeric(commandArgs(trailingOnly = TRUE)[1]) Ny <- as.numeric(commandArgs(trailingOnly = TRUE)[2]) Nz <- as.numeric(commandArgs(trailingOnly = TRUE)[3]) # m <- data.matrix(read.table("Numbers.txt",header=FALSE,sep="")) m <-readBin("Numbers.txt",double(),n=Nx*Ny*Nz,endian="little") A<-array(m,c(Nx,Ny,Nz)) plot3d(slice.index(A,1),slice.index(A,2),slice.index(A,3),col=rainbow(256)[A/(max(A))*256+1],alpha=ifelse(A!=0,1,0)) rgl.viewpoint(theta=30,phi=30) rgl.snapshot("Array.png")
- シェルスクリプトはほぼそのまま
#!/bin/sh Nx=30 Ny=30 Nz=30 gcc -o mat mat.c ./mat $Nx $Ny $Nz R --vanilla --slave --args < mat.R $Nx $Ny $Nz open Array.png # rm Numbers.txt
バイナリで読み書き
- こちらでRの中でC++の関数を使えるようにしている
- そのやり方はわからないが、このときにCとRを使うことを考えていたのでもう少し改良
- CとRの間のファイルのやり取りをバイナリで行う
- Rのバイナリファイル
- Cについてはこちらのなかのバイナリデータ
- Cについての以前の記事
- Cでバイナリファイルの読み書き
- double型の変数が6個
- バイナリで書かれたtest.txtも出力される
// mat.c # include <stdio.h> # include <stdlib.h> int main(void) { double x[]={0.0,1.0,2.0,3.0,4.0,5.0} , y[6]; FILE *fp; fp = fopen("test.txt","w"); if(fp == NULL){ printf("ファイル操作中にエラー"); exit(1); } fwrite(x,sizeof(double),6,fp); fclose(fp); fp = fopen("test.txt","r"); if(fp == NULL){ printf("ファイル操作中にエラー"); exit(1); } fread(y,sizeof(double),6,fp); fclose(fp); // 和を出力させている printf("%lf",y[0]+y[1]+y[2]+y[3]+y[4]+y[5]); return 0; }
- Rで読み込み
- double型変数6個の読み込み
- readBin()を使う
# ファイルの場所とバイナリモードの読み込みの指定 to.read = file("~/Desktop/read/test.txt","rb") # 読み込み方の指定をする readBin(to.read,double(),n=6,endian = "little")
- Rの実行結果
> to.read = file("~/Desktop/read/test.txt","rb") > readBin(to.read,double(),n=6,endian = "little") [1] 0 1 2 3 4 5
CとRを動かす
- 久しぶりにCの復習をしてみた
- シェルでCとRを動かせるようにシェルスクリプトを書いた
- Cを計算に使いたい
- Rで図を描きたい
- いままでマスで仕切ってマスごとに計算するというシミュレーションをやってきていたので、Cでも同じことをしてみる
- マスの大きさをシェルスクリプトから与えられるようにしてみた
- 下の3つを同じディレクトリに置いておいて、シェルスクリプトを実行すればよい
- 全体の流れとしては
#!/bin/sh Nx=30 Ny=30 Nz=30 # Cをコンパイル、実行まで gcc -o mat mat.c ./mat $Nx $Ny $Nz # Rを実行 R --vanilla --slave --args < mat.R $Nx $Ny $Nz # ファイルの実行と消去 open Array.png rm Numbers.txt
/* mat.c */ #include <stdio.h> #include <math.h> #include <stdlib.h> #define PI 3.1415926535 int main (int argc, char *argv[]){ int Nx, Ny, Nz; int i,j,k; FILE *fpA; Nx = atoi(argv[1]); Ny = atoi(argv[2]); Nz = atoi(argv[3]); double A[Nx][Ny][Nz]; for (k = 0; k < Nz; k++) { for (j = 0; j < Ny; j++) { for (i = 0; i < Nx; i++) { A[i][j][k] = (i + 1)*(j + 1)*(k + 1)*1.0; fpA = fopen("Numbers.txt","a"); if(fpA == NULL)return 1; fprintf(fpA,"%f\n",A[i][j][k]); fclose(fpA); }}} return 0; }
# mat.R library(rgl) Nx <- as.numeric(commandArgs(trailingOnly = TRUE)[1]) Ny <- as.numeric(commandArgs(trailingOnly = TRUE)[2]) Nz <- as.numeric(commandArgs(trailingOnly = TRUE)[3]) m <- data.matrix(read.table("Numbers.txt",header=FALSE,sep="")) A<-array(m,c(Nx,Ny,Nz)) plot3d(slice.index(A,1),slice.index(A,2),slice.index(A,3),col=rainbow(256)[A/(max(A))*256+1],alpha=ifelse(A!=0,1,0)) rgl.snapshot("Array.png")
ローレンツアトラクタ
# ローレンツ方程式 p<-10 r<-28 b<-8/3 f<-function(x,y,z){-p*x+p*y} g<-function(x,y,z){-x*z+r*x-y} h<-function(x,y,z){x*y-b*z} # 平衡点を求める # 初期の値 x<-10 y<-10 z<-10 T<-100 d<-0.01 for(t in 1:T){ A<-matrix(c( (f(x+d,y,z)-f(x-d,y,z))/(2*d),(f(x,y+d,z)-f(x,y-d,z))/(2*d),(f(x,y,z+d)-f(x,y,z-d))/(2*d), (g(x+d,y,z)-g(x-d,y,z))/(2*d),(g(x,y+d,z)-g(x,y-d,z))/(2*d),(g(x,y,z+d)-g(x,y,z-d))/(2*d), (h(x+d,y,z)-h(x-d,y,z))/(2*d),(h(x,y+d,z)-h(x,y-d,z))/(2*d),(h(x,y,z+d)-h(x,y,z-d))/(2*d) ),byrow=T,3,3) dX<- -solve(A)%*%c(f(x,y,z),g(x,y,z),h(x,y,z)) x<-x+dX[1] y<-y+dX[2] z<-z+dX[3] } x;y;z f(x,y,z);g(x,y,z);h(x,y,z) # 確認 # 軌跡を書いてみる library(rgl) x<-0.1;y<-0;z<-0 V<-matrix(c(x,y,z),3,1) dt<-0.01 T<-100 Nt<-T/dt for(t in 1:Nt){ dX<-c(f(x,y,z),g(x,y,z),h(x,y,z))*dt x<-x+dX[1] y<-y+dX[2] z<-z+dX[3] V<-cbind(V,c(x,y,z)) } plot3d(t(V))
library(rgl) # 平行移動と拡大縮小で(0,1)におさめる U<-V U[1,]<-(V[1,]-min(V[1,]))/(max(V[1,])-min(V[1,])) U[2,]<-(V[2,]-min(V[2,]))/(max(V[2,])-min(V[2,])) U[3,]<-(V[3,]-min(V[3,]))/(max(V[3,])-min(V[3,])) plot3d(t(U),xlim=c(0,1),ylim=c(0,1),zlim=c(0,1)) # 精度を与えてデータを集計する L<-40 M<-array(0,c(L,L,L)) for(l in 1:dim(U)[2]){ i<-floor(U[1,l]*L) j<-floor(U[2,l]*L) k<-floor(U[3,l]*L) M[i,j,k]<-M[i,j,k]+1 } plot3d(slice.index(M,1),slice.index(M,2),slice.index(M,3),alpha=ifelse(M==0,0,1)) # このままでは重いので点のあるところのみを選んでプロット M2<-rbind((which(M > 0)-1) %% L,(which(M > 0)-1) %% L^2,(which(M > 0)-1) %% L^3)+1 plot3d(t(M2))
# 各位置での速度を計算する Nx<-Ny<-Nz<-40 v1<-seq(from=min(V[1,],to=max(V[1,])),length=Nx) v2<-seq(from=min(V[2,],to=max(V[2,])),length=Ny) v3<-seq(from=min(V[3,],to=max(V[3,])),length=Nz) # 各位置での速度を計算する F<-array(0,c(Nx,Ny,Nz,3)) for(x in 1:Nx){ for(y in 1:Ny){ for(z in 1:Nz){ lx<-v1[x] ly<-v2[y] lz<-v3[z] F[x,y,z,1]<-f(lx,ly,lz) F[x,y,z,2]<-g(lx,ly,lz) F[x,y,z,3]<-h(lx,ly,lz) }}} # 速度を色にしてプロットする Col1<-(F[,,,1]-min(F[,,,1]))/(max(F[,,,1])-min(F[,,,1])) Col2<-(F[,,,2]-min(F[,,,2]))/(max(F[,,,2])-min(F[,,,2])) Col3<-(F[,,,3]-min(F[,,,3]))/(max(F[,,,3])-min(F[,,,3])) plot3d(v1[slice.index(F,1)],v2[slice.index(F,2)],v3[slice.index(F,3)],xlab="x",ylab="y",zlab="z",col=rainbow(101)[Col1*100+1],main="velocity x") plot3d(v1[slice.index(F,1)],v2[slice.index(F,2)],v3[slice.index(F,3)],xlab="x",ylab="y",zlab="z",col=rainbow(101)[Col2*100+1],main="velocity y") plot3d(v1[slice.index(F,1)],v2[slice.index(F,2)],v3[slice.index(F,3)],xlab="x",ylab="y",zlab="z",col=rainbow(101)[Col3*100+1],main="velocity z") # 偏微分係数を計算してプロット # z方向について Fz<-F[,,-1,3]-F[,,-Nz,3] err<-0.000001 if(max(Fz) - min(Fz) < err){ ColFz<-1 }else{ ColFz<-(Fz-min(Fz))/(max(Fz)-min(Fz)) } plot3d(v1[slice.index(Fz,1)],v2[slice.index(Fz,2)],v3[slice.index(Fz,3)],xlab="x",ylab="y",zlab="z",col=rainbow(101)[ColFz*100+1],main="Fz")
# 時系列データから速度を計算し色にしてプロット du1<-U[1,-1]-U[1,-length(U[1,])] du1<-(du1-min(du1))/(max(du1)-min(du1)) du2<-U[2,-1]-U[2,-length(U[2,])] du2<-(du2-min(du2))/(max(du2)-min(du2)) du3<-U[3,-3]-U[3,-length(U[3,])] du3<-(du3-min(du3))/(max(du3)-min(du3)) C1<-c(du1[1],du1*100+1) C2<-c(du2[1],du2*100+1) C3<-c(du3[1],du3*100+1) plot3d(U[1,],U[2,],U[3,],col=rainbow(101)[C1]) plot3d(U[1,],U[2,],U[3,],col=rainbow(101)[C2]) plot3d(U[1,],U[2,],U[3,],col=rainbow(101)[C3])